オーチャードグラスの品種識別に有用なSSRプライマー対及びその利用
【課題】簡便、迅速かつ正確なオーチャードグラスの品種識別に有用なSSRプライマー対、マーカー遺伝子、及び品種識別方法を提供する。
【解決手段】オーチャードグラスのゲノム上のSSR領域の両側の塩基配列を用いて設計したプライマー対、該プライマー対を利用してPCR増幅した増幅産物からなる特定マーカー遺伝子、及び識別対象となるオーチャードグラスのバルクDNAを使用することで、個体間の遺伝子のばらつきを無くし、品種特異的なSSRをPCRで特異的に増幅させ、増幅された特定マーカー遺伝子断片の長さの違いを検出することで、品種の識別を行う、オーチャードグラス14品種の品種識別方法。
【解決手段】オーチャードグラスのゲノム上のSSR領域の両側の塩基配列を用いて設計したプライマー対、該プライマー対を利用してPCR増幅した増幅産物からなる特定マーカー遺伝子、及び識別対象となるオーチャードグラスのバルクDNAを使用することで、個体間の遺伝子のばらつきを無くし、品種特異的なSSRをPCRで特異的に増幅させ、増幅された特定マーカー遺伝子断片の長さの違いを検出することで、品種の識別を行う、オーチャードグラス14品種の品種識別方法。
【発明の詳細な説明】
【技術分野】
【0001】
本発明は、オーチャードグラスの品種の識別のために、特定のSSR領域を増幅させる遺伝子増幅用プライマーのFプライマー及びRプライマー対及びその利用に関するものであり、更に詳しくは、オーチャードグラス14品種を識別することを可能とする、特定のSSR領域を増幅させるための遺伝子増幅用のFプライマー及びRプライマー対、該プライマー対からPCR増幅させた識別対象の遺伝子の特定マーカーの塩基配列、該マーカーを利用してオーチャードグラスの品種を識別する方法に関するものである。本発明は、オーチャードグラスの品種識別用のSSRプライマー、該プライマーを利用してオーチャードグラスのゲノムDNAをPCR増幅させ、その増幅断片のマーカーを比較することで品種を識別することを可能とするオーチャードグラス品種の識別方法に関する新技術・新製品を提供するものである。
【背景技術】
【0002】
オーチャードグラス(Dactylis glomerata L.)は、寒地型牧草として利用される多年生イネ科の植物である。牧草として利用されているオーチャードグラス品種の大半は、4倍体(2n=28)である。
【0003】
先行技術として、主に飼料作物として利用される他殖性のイネ科牧草の品種識別法としては、イタリアンライグラスにおいて、12品種を識別する方法が開発されている(特許文献1参照)。
【0004】
この方法は、イタリアンライグラスのゲノム上のSSR(Simple Sequence Repeats)領域をPCRで増幅させ、増幅された断片の長さの違いを検出することで品種を識別するものである。しかし、オーチャードグラスにおいては、このような品種識別法が開発されていない。
【0005】
このため、オーチャードグラスの品種識別は、これまで、圃場での特性調査により行われてきた。圃場での特性調査とは、例えば、一検体につき10個体6反復計60個体を栽培し、草丈、出穂月日、草型、葉身長等の形質を調査し、共に栽培した60個体の標準個体と比較して同品種かどうか判定を行う方法である。しかしながら、このような圃場での特性調査は、1)調査のための圃場が必要である、2)調査に多くの労力が必要である、3)調査結果が判明するまでに多くの時間が必要である、等の問題点がある。
【先行技術文献】
【特許文献】
【0006】
【特許文献1】特開2008−237180号公報
【発明の概要】
【発明が解決しようとする課題】
【0007】
このような状況の中で、本発明者らは、上記従来技術に鑑みて、短期間で、簡便且つ正確にオーチャードグラス14品種を識別できる新しい手法を開発することを目標として鋭意研究を重ねた結果、オーチャードグラスのゲノム上におけるSSR領域の両側の塩基配列を用いて作成したプライマーから増幅されるマーカーを用いることにより所期の目的を達成し得ることを見出し、更に研究を重ねて、本発明を完成するに至った。
【0008】
本発明は、複数個体のDNAを混合するバルクDNAをテンプレートDNAとしたオーチャードグラスの品種識別を可能にするPCR(polymerase chain reaction)用のSSRプライマー対を提供することを目的とするものである。
【0009】
本発明は、労力及び時間が必要な従来の圃場での特性調査に代わり、短期間で、簡便且つ正確にオーチャードグラスの品種識別を可能にするPCR用のプライマー対、該プライマー対からPCR増幅させた識別対象の遺伝子の特定マーカーの塩基配列、該マーカーを利用したオーチャードグラスの品種識別方法を提供することを目的とするものである。
【課題を解決するための手段】
【0010】
上記課題を解決するための本発明は、以下の技術的手段から構成される。
(1)オーチャードグラスの品種識別用のプライマーであって、オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマー対。
(2)オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマーのF(Forward)プライマー及びR(Reverse)プライマーからなる、前記(1)に記載のプライマー対。
(3)オーチャードグラスのゲノム上におけるSSR領域の両端の塩基配列を用いて設計した遺伝子増幅用プライマー対であって、配列表の配列番号1〜15のF(Forward)プライマー及び配列番号16〜30のR(Reverse)プライマーを1対とするプライマー対である、前記(1)に記載のプライマー対。
(4)前記(2)に記載のプライマー対の単数又は複数の組合せからなることを特徴とするオーチャードグラスの品種識別用プライマーセット。
(5)オーチャードグラスのゲノム上におけるSSR領域を増幅する前記(1)から(4)のいずれかに記載のプライマーからPCR増幅させた特定の増幅産物からなることを特徴とするマーカー遺伝子。
(6)前記(5)に記載のマーカー遺伝子であって、配列表の配列番号31〜45のいずれかの塩基配列を有することを特徴とするマーカー遺伝子。
(7)前記(5)又は(6)に記載のマーカー遺伝子を使用し、識別対象のオーチャードグラスDNAのPCR増幅の増幅産物の多型を確認することで品種の識別を行うことを特徴とするオーチャードグラスの品種識別方法。
(8)識別対象のオーチャードグラス遺伝子のPCR増幅産物のサイズ又はバンドパターンに基づいて、品種の識別を行うことを特徴とするオーチャードグラス品種識別方法。
(9)対象品種のバルクDNAをテンプレートDNAとして使用したオーチャードグラス遺伝子のPCRによる増幅を行い、同時に、数品種の識別を行う、前記(7)又は(8)に記載の方法。
(10)アキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種からなるオーチャードグラス品種を識別する、前記(7)〜(9)のいずれかに記載の品種識別方法。
【0011】
次に、本発明について更に詳細に説明する。
本発明は、オーチャードグラスの品種識別用のプライマーであって、オーチャードグラスのゲノム上におけるSSR領域を増幅させるための遺伝子増幅用プライマー対の点に特徴を有するものである。また、本発明は、オーチャードグラスの品種識別方法であって、オーチャードグラスのゲノム上におけるSSR領域を増幅する上記のプライマーから増幅される特定マーカーを使用し、識別対象のオーチャードグラスDNAのPCRによる増幅を行い、その増幅産物の多型を確認することで、品種の識別を行うことを特徴とするものである。
【0012】
本発明では、オーチャードグラスのゲノム上におけるSSR領域の両側の塩基配列を用いて設計したプライマー対から、識別対象のオーチャードグラス遺伝子の特定マーカーをPCR増幅し、そのマーカーサイズ、及びバンドパターン(複数の遺伝子座のバンドの有無による組み合わせ)を確認することで、品種を識別する。
【0013】
対象品種のバルクDNAを使用することで、1個体毎の解析を行わないため、オーチャードグラスの遺伝子のPCRによる増幅を行い、同時に、数品種の解析が行える。すなわち、本発明では、個体単位での解析が不要となるため、対象品種のバルクDNAを使用したオーチャードグラス遺伝子のPCRによる増幅を行い、同時に、数品種の識別を行う。他殖性であるオーチャードグラスは、遺伝的に個体間で異なるが、バルクDNAをテンプレートとして用いることで、品種の非特異的な個体間の差異を無くし、かつ効率よく品種の識別が可能となる。
【0014】
本発明により、オーチャードグラス品種を識別するオーチャードグラスのSSRマーカーが提供され、単数又は複数のプライマー対を使用したPCRによる識別対象の遺伝子を増幅させ、そのマーカーのサイズ及びバンドパターンを検証することにより、オーチャードグラスのアキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種の品種識別を行うことができる。
【0015】
本発明では、2〜4塩基が高頻度に繰り返された配列からなるSSR領域の両側を挟むように設計した遺伝子増幅用プライマーの15対(表1参照)で、単数又は複数のプライマー対を使用し、対象となるオーチャードグラス14品種について、PCR増幅を行い、その増幅断片を比較することで、品種を識別する。
【0016】
本発明では、実際の使用時に、バルクDNAをテンプレートとすることを想定し、品種特異的なSSRマーカーを選抜するため、対象品種のゲノムDNAを複数個体混合するバルクしたDNAをテンプレートとすることにより識別が行われる。そのため、本発明では、例えば、濃度を一定にしたオーチャードグラスDNAを10個体合わせて、バルクDNAテンプレートとして使用する。
【0017】
本発明で使用されるSSRプライマー対は、プライマー設計ソフトウエア「primer 0.5,ftp://ftp−genome.wi.mit.edu/distribution/software/primer0.5」を使用して作成した。本発明のオーチャードグラスの品種識別に有用なプライマー対の配列を、次の表1に示す。
【0018】
【表1】

【0019】
次に、上記表1の配列のプライマー対の14品種内での増幅型の詳細について説明する(表2参照)。
【0020】
プライマー「OG202」は、ハルジマン及びトヨミドリを識別するプライマー対で、230bp付近で、ハルジマンに特異的な増幅を示し、145〜175bpの間に、トヨミドリ特有の増幅を示し、品種特異的な増幅があることを示す。
【0021】
プライマー「OG261」は、ベンチマークを識別するプライマー対で、230bp付近に、ベンチマークに特異的な増幅を示す。
【0022】
プライマー「OG264」は、マキバミドリを識別するプライマー対で、230から255bpの間で、マキバミドリに特異的な増幅を示す。
【0023】
プライマー「OG357」は、145bp付近の増幅パターンの違い、すなわち、品種特異的なバンドパターンによって、フロンティア及びポトマックの識別を行うことができる。「OG806」及び「OG965」と比較することが必要となる。
【0024】
プライマー「OG474」は、オカミドリを識別するプライマー対で、145〜175bpの間で、オカミドリに特異的な増幅を示す。
【0025】
プライマー「OG493」は、アキミドリIIを識別するプライマー対であって、145〜175bpの間で、アキミドリIIに特異的な増幅を示す。「OG954」と併用することで、識別能を向上させることができる。
【0026】
プライマー「OG503」は、はるねみどりを識別するプライマー対で、200bp付近で、はるねみどりに特異的な増幅を示す。
【0027】
プライマー「OG654」は、ワセミドリを識別するプライマー対で、145bp付近で、ワセミドリに特異的な増幅を示す。
【0028】
プライマー「OG670」は、ナツミドリを識別するプライマー対で、100bp付近で、ナツミドリに特異的な増幅を示す。
【0029】
プライマー「OG757」は、まきばたろうを識別するプライマー対で、120bp付近で、まきばたろうに特異的な増幅を示す。「OG827」と併用することで、識別能を向上させることができる。
【0030】
プライマー「OG785」は、キタミドリを識別するプライマー対で、176bp付近で、キタミドリに特異的な増幅を示す。
【0031】
プライマー「OG806」は、145bp付近の増幅パターンの違い、すなわち、品種特異的な増幅があることによって、フロンティア及びポトマックの識別を行うことができる。「OG806」及び「OG965」と比較することが必要となる。
【0032】
プライマー「OG827」は、まきばたろうを識別するプライマー対で、204bp付近で、まきばたろうに特異的な増幅を示す。「OG757」と併用することで、識別能を向上させることができる。
【0033】
プライマー「OG954」は、アキミドリII及びバッカスを識別するプライマー対で、175〜200bpの間で、アキミドリII特有の増幅を示し、175bp付近で、バッカスに特異的な増幅を示す。アキミドリIIについては、「OG954」と併用することで、識別能を向上させることができる。
【0034】
プライマー「OG965」は、175bp付近の増幅で、フロンティアとポトマック間の区別性を示す。「OG806」及び「OG965」と比較することが必要となる。
【0035】
上述のプライマー対を、14品種で比較した場合に見られるバンドパターンを、次の表2にまとめて示す。
【0036】
【表2】

【発明の効果】
【0037】
本発明により、次のような効果が奏される。
(1)本発明により、オーチャードグラスの品種を識別するオーチャードグラスのSSRマーカーが提供される。
(2)単数又は複数のプライマー対を使用したPCRによる識別対象の遺伝子を増幅させ、そのマーカーのサイズ及びバンドパターンを検証することにより、オーチャードグラスの品種識別を行うことができる。
(3)本発明により、アキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、からなる14品種相互での品種識別を行うことができる。
(4)個体単位の解析ではなく、複数個体のDNAを混合するバルクDNAをテンプレートDNAとすることにより、解析時間の短縮及び正確な品種識別が可能となる。
【図面の簡単な説明】
【0038】
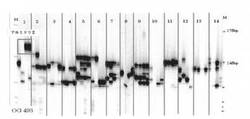
【図1】実施例におけるOG493を用いたPCRの電気泳動の結果を示す。Mは、サイズマーカーを示し、そのサイズを右端にbpで記載する。それぞれの品種4サンプルの電気泳動の結果を示す。図2〜15も同様である。
【図2】実施例におけるOG954を用いたPCRの電気泳動の結果を示す。
【図3】実施例におけるOG785を用いたPCRの電気泳動の結果を示す。
【図4】実施例におけるOG670を用いたPCRの電気泳動の結果を示す。
【図5】実施例におけるOG474を用いたPCRの電気泳動の結果を示す。
【図6】実施例におけるOG654を用いたPCRの電気泳動の結果を示す。
【図7】実施例におけるOG202を用いたPCRの電気泳動の結果を示す。
【図8】実施例におけるOG264を用いたPCRの電気泳動の結果を示す。
【図9】実施例におけるOG261を用いたPCRの電気泳動の結果を示す。
【図10】実施例におけるOG503を用いたPCRの電気泳動の結果を示す。
【図11】実施例におけるOG357を用いたPCRの電気泳動の結果を示す。
【図12】実施例におけるOG806を用いたPCRの電気泳動の結果を示す。
【図13】実施例におけるOG965を用いたPCRの電気泳動の結果を示す。
【図14】実施例におけるOG757を用いたPCRの電気泳動の結果を示す。
【図15】実施例におけるOG827を用いたPCRの電気泳動の結果を示す。
【図16】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【図17】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【図18】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【図19】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【発明を実施するための形態】
【0039】
次に、本発明を実施例に基づいて具体的に説明するが、本発明は、以下の実施例によって何ら限定されるものではない。
【実施例】
【0040】
国内で育成されたオーチャードグラスのアキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種から、CTAB法を用いて、ゲノムDNAを抽出した。
【0041】
抽出したDNA溶液は、滅菌水でDNA濃度を20ng/μlに調整し、10個体を混合し、バルクにしたものを、PCR用のテンプレートDNAとして用いた。
【0042】
本実施例で使用した機器は、以下の通りである。
すなわち、本実施例では、T GRADIENT Themocycler(Biometra)、TaKaRa PCR Thermal Cycler TP600(タカラバイオ株式会社)、i Cycler(BIO−RAD)、及び、Gene Amp PCR System 9700(ABI)、DNAシーケンシングシステムLIC−4200L(s)(LI−COR)を用いた。
【0043】
<50%アクリルアミドゲル>
本実施例で使用した試薬は、以下の通りである。
アクリルアミドゲルとして、尿素(和光純薬工業株式会社)、Long Ranger Gel solution DNA Sequencing用(タカラバイオ株式会社)、10xTBE buffer、10%APS、TEMED(和光純薬工業株式会社)、を用いた。
【0044】
<PCR反応液>
PCR反応液として、Gene Taq NT(和光純薬工業株式会社)もしくはTaq DNA Polymerase(BIO NEER)、1pmol/μl M13 Forward(−29)Primer:IRD700もしくはIRD800の蛍光標識を含む(日清紡)、を用いた。サイズマーカーとして、50−350bp SIZING STANDARD−BULK(LI−COR)を使用した。本発明では、LI−CORのプロトコールに基づいて、ゲルと色素マーカーの作製を行った。
【0045】
<PCR反応液:計10μlの調製>
PCR反応液の調製は、以下の通りとした。
トールフェスク対象品種から抽出したバルクDNA:1μl
10xGene Taq Universal buffer:1μl
2.5mM dNTP Mixture:0.8μl
ddH2O:6.5μl
Primer Forward(20pmol/μl):0.06μl
Primer Reverse(20pmol/μl):0.3μl
M13 Forward(−29) Primer:0.3μl
Gene Taq NT(5 unit/μl):0.1μl
BIO NEERのTaq DNA Polymeraseを使用する場合にも、同様にPCR反応液を調製した。
【0046】
<PCR条件>
PCR条件は、以下の通りとした。
95℃1分−65℃1分−72℃1分30秒(2サイクル)95℃1分−65℃1分−72℃1分30秒(10サイクル。1サイクルごとに65℃を1℃ずつ下げていく)95℃1分−55℃1分−72℃1分30秒(30サイクル)で反応させた。PCR増幅産物は、色素マーカー5μlを加え、90℃3分のディネーチャーを行った後、遮光し、氷上で1時間以上静置させることで安定させた後、アクリルアミドゲルを使用して、電気泳動を行い、マーカーの増幅を確認した。
【0047】
本実施例では、特に記載しない限り、オーチャードグラスのアキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種を、テンプレートとして使用した。
【0048】
本実施例では、オーチャードグラスの14品種それぞれのバルクしたDNAを、4サンプル使用して、電気泳動を行い、14品種を同時に比較した(図1〜15)。
【0049】
プライマー「OG493」を使用し、PCRを行った。その電気泳動の結果を図1に示す。このプライマー対は、145〜175bpの間で、アキミドリIIに特異的な増幅を示し、アキミドリIIの識別に有効であった。プライマー「OG954」を併用することで、識別精度が向上した。
【0050】
プライマー「OG954」を使用し、PCRを行った。その電気泳動の結果を図2に示す。このプライマー対は、175〜200bpの間で、アキミドリII特有の増幅を示し、175bp付近で、バッカスに特異的な増幅を示し、2品種の識別に有効であった。アキミドリIIについては、プライマー「OG493」を併用することで、識別精度が向上した。
【0051】
プライマー「OG785」を使用し、PCRを行った。その電気泳動の結果を図3に示す。このプライマー対は、176bp付近で、キタミドリに特異的な増幅を示し、キタミドリの識別に有効であった。
【0052】
プライマー「OG670」を使用し、PCRを行った。その電気泳動の結果を図4に示す。このプライマー対は、100bp付近で、ナツミドリに特異的な増幅を示し、ナツミドリの識別に有効であった。
【0053】
プライマー「OG474」を使用し、PCRを行った。その電気泳動の結果を図5に示す。このプライマー対は、145〜175bpの間で、オカミドリに特異的な増幅を示し、オカミドリの識別に有効であった。キタミドリによく似たサイズの増幅が見られることから、キタミドリのバルクDNAをスタンダードとして、同時に泳動し、比較することが必要になる。
【0054】
プライマー「OG654」を使用し、PCRを行った。その電気泳動の結果を図6に示す。このプライマー対は、145bp付近で、ワセミドリに特異的な増幅を示し、ワセミドリの識別に有効であった。
【0055】
プライマー「OG202」を使用し、PCRを行った。その電気泳動の結果を図7に示す。このプライマー対では、230bp付近で、ハルジマンに特異的な増幅を示し、145〜175bpの間に、トヨミドリ特有の増幅を示し、これらの2品種の識別に有効であった。
【0056】
プライマー「OG264」を使用し、PCRを行った。その電気泳動の結果を図8に示す。このプライマー対は、230から255bpの間で、マキバミドリに特異的な増幅を示し、マキバミドリの識別に有効であった。
【0057】
プライマー「OG261」を使用し、PCRを行った。その電気泳動の結果を図9に示す。このプライマー対は、230bp付近で、ベンチマークに特異的な増幅を示し、ベンチマークの識別に有効であった。
【0058】
プライマー「OG503」を使用し、PCRを行った。その電気泳動の結果を図10に示す。このプライマー対は、200bp付近で、はるねみどりに特異的な増幅を示し、はるねみどりの識別に有効であった。
【0059】
プライマー「OG357」を使用し、PCRを行った。その電気泳動の結果を図11に示す。このプライマー対は、145bp付近の増幅パターンの違いによって、フロンティア及びポトマックの識別に有効であった。プライマー「OG806」及び「OG965」を併用することで、精度を向上させることができる。
【0060】
プライマー「OG806」を使用し、PCRを行った。その電気泳動の結果を図12に示す。このプライマー対は、145bp付近の増幅パターンの違いによって、フロンティア及びポトマックの識別を行うことができた。プライマー「OG357」及び「OG965」を併用することで、精度を向上させることができる。
【0061】
プライマー「OG965」を使用し、PCRを行った。その電気泳動の結果を図13に示す。このプライマー対は、175bp付近の増幅でフロンティアとポトマック間の区別性を示し、フロンティア及びポトマックの識別に有効であった。プライマー「OG357」及び「OG806」を併用することで、精度を向上させることができる。
【0062】
プライマー「OG757」を使用し、PCRを行った。その電気泳動の結果を図14に示す。このプライマー対は、120bp付近で、まきばたろうに特異的な増幅を示し、まきばたろうの識別に有効であった。プライマー「OG827」を併用することで、識別精度が向上した。
【0063】
「OG827」を使用しPCRを行った。その電気泳動の結果を図15に示す。このプライマー対は、204bp付近で、まきばたろうに特異的な増幅を示し、まきばたろうの識別に有効であった。プライマー「OG757」を併用することで、識別精度が向上した。本発明のプライマーで増幅した特定マーカー遺伝子の塩基配列を、図16〜19に示す。
【産業上の利用可能性】
【0064】
以上詳述したように、本発明は、オーチャードグラスの品種識別に有用なSSRプライマー対及びその利用に係るものであり、本発明により、オーチャードグラス14品種の特定のSSR領域を増幅させるための遺伝子増幅用プライマーのFプライマー及びRプライマー対を提供することができる。また、本発明は、単数又は複数のプライマー対を使用したPCRにより識別対象の遺伝子を増幅させてなるマーカー遺伝子を提供することができ、そのマーカー遺伝子のサイズ及びバンドパターンを検証することにより、オーチャードグラスの品種識別を行うことができる。本発明により、オーチャードグラスの14品種相互での品種識別を行うことができる。本発明は、短い時間で、正確なオーチャードグラスの品種識別を可能にする新しい品種識別方法を提供するものとして有用である。
【符号の説明】
【0065】
1 アキミドリII
2 キタミドリ
3 ナツミドリ
4 バッカス
5 オカミドリ
6 ワセミドリ
7 ハルジマン
9 マキバミドリ
10 トヨミドリ
11 ベンチマーク
12 はるねみどり
13 フロンティア
14 ポトマック
15 まきばたろう
【技術分野】
【0001】
本発明は、オーチャードグラスの品種の識別のために、特定のSSR領域を増幅させる遺伝子増幅用プライマーのFプライマー及びRプライマー対及びその利用に関するものであり、更に詳しくは、オーチャードグラス14品種を識別することを可能とする、特定のSSR領域を増幅させるための遺伝子増幅用のFプライマー及びRプライマー対、該プライマー対からPCR増幅させた識別対象の遺伝子の特定マーカーの塩基配列、該マーカーを利用してオーチャードグラスの品種を識別する方法に関するものである。本発明は、オーチャードグラスの品種識別用のSSRプライマー、該プライマーを利用してオーチャードグラスのゲノムDNAをPCR増幅させ、その増幅断片のマーカーを比較することで品種を識別することを可能とするオーチャードグラス品種の識別方法に関する新技術・新製品を提供するものである。
【背景技術】
【0002】
オーチャードグラス(Dactylis glomerata L.)は、寒地型牧草として利用される多年生イネ科の植物である。牧草として利用されているオーチャードグラス品種の大半は、4倍体(2n=28)である。
【0003】
先行技術として、主に飼料作物として利用される他殖性のイネ科牧草の品種識別法としては、イタリアンライグラスにおいて、12品種を識別する方法が開発されている(特許文献1参照)。
【0004】
この方法は、イタリアンライグラスのゲノム上のSSR(Simple Sequence Repeats)領域をPCRで増幅させ、増幅された断片の長さの違いを検出することで品種を識別するものである。しかし、オーチャードグラスにおいては、このような品種識別法が開発されていない。
【0005】
このため、オーチャードグラスの品種識別は、これまで、圃場での特性調査により行われてきた。圃場での特性調査とは、例えば、一検体につき10個体6反復計60個体を栽培し、草丈、出穂月日、草型、葉身長等の形質を調査し、共に栽培した60個体の標準個体と比較して同品種かどうか判定を行う方法である。しかしながら、このような圃場での特性調査は、1)調査のための圃場が必要である、2)調査に多くの労力が必要である、3)調査結果が判明するまでに多くの時間が必要である、等の問題点がある。
【先行技術文献】
【特許文献】
【0006】
【特許文献1】特開2008−237180号公報
【発明の概要】
【発明が解決しようとする課題】
【0007】
このような状況の中で、本発明者らは、上記従来技術に鑑みて、短期間で、簡便且つ正確にオーチャードグラス14品種を識別できる新しい手法を開発することを目標として鋭意研究を重ねた結果、オーチャードグラスのゲノム上におけるSSR領域の両側の塩基配列を用いて作成したプライマーから増幅されるマーカーを用いることにより所期の目的を達成し得ることを見出し、更に研究を重ねて、本発明を完成するに至った。
【0008】
本発明は、複数個体のDNAを混合するバルクDNAをテンプレートDNAとしたオーチャードグラスの品種識別を可能にするPCR(polymerase chain reaction)用のSSRプライマー対を提供することを目的とするものである。
【0009】
本発明は、労力及び時間が必要な従来の圃場での特性調査に代わり、短期間で、簡便且つ正確にオーチャードグラスの品種識別を可能にするPCR用のプライマー対、該プライマー対からPCR増幅させた識別対象の遺伝子の特定マーカーの塩基配列、該マーカーを利用したオーチャードグラスの品種識別方法を提供することを目的とするものである。
【課題を解決するための手段】
【0010】
上記課題を解決するための本発明は、以下の技術的手段から構成される。
(1)オーチャードグラスの品種識別用のプライマーであって、オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマー対。
(2)オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマーのF(Forward)プライマー及びR(Reverse)プライマーからなる、前記(1)に記載のプライマー対。
(3)オーチャードグラスのゲノム上におけるSSR領域の両端の塩基配列を用いて設計した遺伝子増幅用プライマー対であって、配列表の配列番号1〜15のF(Forward)プライマー及び配列番号16〜30のR(Reverse)プライマーを1対とするプライマー対である、前記(1)に記載のプライマー対。
(4)前記(2)に記載のプライマー対の単数又は複数の組合せからなることを特徴とするオーチャードグラスの品種識別用プライマーセット。
(5)オーチャードグラスのゲノム上におけるSSR領域を増幅する前記(1)から(4)のいずれかに記載のプライマーからPCR増幅させた特定の増幅産物からなることを特徴とするマーカー遺伝子。
(6)前記(5)に記載のマーカー遺伝子であって、配列表の配列番号31〜45のいずれかの塩基配列を有することを特徴とするマーカー遺伝子。
(7)前記(5)又は(6)に記載のマーカー遺伝子を使用し、識別対象のオーチャードグラスDNAのPCR増幅の増幅産物の多型を確認することで品種の識別を行うことを特徴とするオーチャードグラスの品種識別方法。
(8)識別対象のオーチャードグラス遺伝子のPCR増幅産物のサイズ又はバンドパターンに基づいて、品種の識別を行うことを特徴とするオーチャードグラス品種識別方法。
(9)対象品種のバルクDNAをテンプレートDNAとして使用したオーチャードグラス遺伝子のPCRによる増幅を行い、同時に、数品種の識別を行う、前記(7)又は(8)に記載の方法。
(10)アキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種からなるオーチャードグラス品種を識別する、前記(7)〜(9)のいずれかに記載の品種識別方法。
【0011】
次に、本発明について更に詳細に説明する。
本発明は、オーチャードグラスの品種識別用のプライマーであって、オーチャードグラスのゲノム上におけるSSR領域を増幅させるための遺伝子増幅用プライマー対の点に特徴を有するものである。また、本発明は、オーチャードグラスの品種識別方法であって、オーチャードグラスのゲノム上におけるSSR領域を増幅する上記のプライマーから増幅される特定マーカーを使用し、識別対象のオーチャードグラスDNAのPCRによる増幅を行い、その増幅産物の多型を確認することで、品種の識別を行うことを特徴とするものである。
【0012】
本発明では、オーチャードグラスのゲノム上におけるSSR領域の両側の塩基配列を用いて設計したプライマー対から、識別対象のオーチャードグラス遺伝子の特定マーカーをPCR増幅し、そのマーカーサイズ、及びバンドパターン(複数の遺伝子座のバンドの有無による組み合わせ)を確認することで、品種を識別する。
【0013】
対象品種のバルクDNAを使用することで、1個体毎の解析を行わないため、オーチャードグラスの遺伝子のPCRによる増幅を行い、同時に、数品種の解析が行える。すなわち、本発明では、個体単位での解析が不要となるため、対象品種のバルクDNAを使用したオーチャードグラス遺伝子のPCRによる増幅を行い、同時に、数品種の識別を行う。他殖性であるオーチャードグラスは、遺伝的に個体間で異なるが、バルクDNAをテンプレートとして用いることで、品種の非特異的な個体間の差異を無くし、かつ効率よく品種の識別が可能となる。
【0014】
本発明により、オーチャードグラス品種を識別するオーチャードグラスのSSRマーカーが提供され、単数又は複数のプライマー対を使用したPCRによる識別対象の遺伝子を増幅させ、そのマーカーのサイズ及びバンドパターンを検証することにより、オーチャードグラスのアキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種の品種識別を行うことができる。
【0015】
本発明では、2〜4塩基が高頻度に繰り返された配列からなるSSR領域の両側を挟むように設計した遺伝子増幅用プライマーの15対(表1参照)で、単数又は複数のプライマー対を使用し、対象となるオーチャードグラス14品種について、PCR増幅を行い、その増幅断片を比較することで、品種を識別する。
【0016】
本発明では、実際の使用時に、バルクDNAをテンプレートとすることを想定し、品種特異的なSSRマーカーを選抜するため、対象品種のゲノムDNAを複数個体混合するバルクしたDNAをテンプレートとすることにより識別が行われる。そのため、本発明では、例えば、濃度を一定にしたオーチャードグラスDNAを10個体合わせて、バルクDNAテンプレートとして使用する。
【0017】
本発明で使用されるSSRプライマー対は、プライマー設計ソフトウエア「primer 0.5,ftp://ftp−genome.wi.mit.edu/distribution/software/primer0.5」を使用して作成した。本発明のオーチャードグラスの品種識別に有用なプライマー対の配列を、次の表1に示す。
【0018】
【表1】

【0019】
次に、上記表1の配列のプライマー対の14品種内での増幅型の詳細について説明する(表2参照)。
【0020】
プライマー「OG202」は、ハルジマン及びトヨミドリを識別するプライマー対で、230bp付近で、ハルジマンに特異的な増幅を示し、145〜175bpの間に、トヨミドリ特有の増幅を示し、品種特異的な増幅があることを示す。
【0021】
プライマー「OG261」は、ベンチマークを識別するプライマー対で、230bp付近に、ベンチマークに特異的な増幅を示す。
【0022】
プライマー「OG264」は、マキバミドリを識別するプライマー対で、230から255bpの間で、マキバミドリに特異的な増幅を示す。
【0023】
プライマー「OG357」は、145bp付近の増幅パターンの違い、すなわち、品種特異的なバンドパターンによって、フロンティア及びポトマックの識別を行うことができる。「OG806」及び「OG965」と比較することが必要となる。
【0024】
プライマー「OG474」は、オカミドリを識別するプライマー対で、145〜175bpの間で、オカミドリに特異的な増幅を示す。
【0025】
プライマー「OG493」は、アキミドリIIを識別するプライマー対であって、145〜175bpの間で、アキミドリIIに特異的な増幅を示す。「OG954」と併用することで、識別能を向上させることができる。
【0026】
プライマー「OG503」は、はるねみどりを識別するプライマー対で、200bp付近で、はるねみどりに特異的な増幅を示す。
【0027】
プライマー「OG654」は、ワセミドリを識別するプライマー対で、145bp付近で、ワセミドリに特異的な増幅を示す。
【0028】
プライマー「OG670」は、ナツミドリを識別するプライマー対で、100bp付近で、ナツミドリに特異的な増幅を示す。
【0029】
プライマー「OG757」は、まきばたろうを識別するプライマー対で、120bp付近で、まきばたろうに特異的な増幅を示す。「OG827」と併用することで、識別能を向上させることができる。
【0030】
プライマー「OG785」は、キタミドリを識別するプライマー対で、176bp付近で、キタミドリに特異的な増幅を示す。
【0031】
プライマー「OG806」は、145bp付近の増幅パターンの違い、すなわち、品種特異的な増幅があることによって、フロンティア及びポトマックの識別を行うことができる。「OG806」及び「OG965」と比較することが必要となる。
【0032】
プライマー「OG827」は、まきばたろうを識別するプライマー対で、204bp付近で、まきばたろうに特異的な増幅を示す。「OG757」と併用することで、識別能を向上させることができる。
【0033】
プライマー「OG954」は、アキミドリII及びバッカスを識別するプライマー対で、175〜200bpの間で、アキミドリII特有の増幅を示し、175bp付近で、バッカスに特異的な増幅を示す。アキミドリIIについては、「OG954」と併用することで、識別能を向上させることができる。
【0034】
プライマー「OG965」は、175bp付近の増幅で、フロンティアとポトマック間の区別性を示す。「OG806」及び「OG965」と比較することが必要となる。
【0035】
上述のプライマー対を、14品種で比較した場合に見られるバンドパターンを、次の表2にまとめて示す。
【0036】
【表2】

【発明の効果】
【0037】
本発明により、次のような効果が奏される。
(1)本発明により、オーチャードグラスの品種を識別するオーチャードグラスのSSRマーカーが提供される。
(2)単数又は複数のプライマー対を使用したPCRによる識別対象の遺伝子を増幅させ、そのマーカーのサイズ及びバンドパターンを検証することにより、オーチャードグラスの品種識別を行うことができる。
(3)本発明により、アキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、からなる14品種相互での品種識別を行うことができる。
(4)個体単位の解析ではなく、複数個体のDNAを混合するバルクDNAをテンプレートDNAとすることにより、解析時間の短縮及び正確な品種識別が可能となる。
【図面の簡単な説明】
【0038】
【図1】実施例におけるOG493を用いたPCRの電気泳動の結果を示す。Mは、サイズマーカーを示し、そのサイズを右端にbpで記載する。それぞれの品種4サンプルの電気泳動の結果を示す。図2〜15も同様である。
【図2】実施例におけるOG954を用いたPCRの電気泳動の結果を示す。
【図3】実施例におけるOG785を用いたPCRの電気泳動の結果を示す。
【図4】実施例におけるOG670を用いたPCRの電気泳動の結果を示す。
【図5】実施例におけるOG474を用いたPCRの電気泳動の結果を示す。
【図6】実施例におけるOG654を用いたPCRの電気泳動の結果を示す。
【図7】実施例におけるOG202を用いたPCRの電気泳動の結果を示す。
【図8】実施例におけるOG264を用いたPCRの電気泳動の結果を示す。
【図9】実施例におけるOG261を用いたPCRの電気泳動の結果を示す。
【図10】実施例におけるOG503を用いたPCRの電気泳動の結果を示す。
【図11】実施例におけるOG357を用いたPCRの電気泳動の結果を示す。
【図12】実施例におけるOG806を用いたPCRの電気泳動の結果を示す。
【図13】実施例におけるOG965を用いたPCRの電気泳動の結果を示す。
【図14】実施例におけるOG757を用いたPCRの電気泳動の結果を示す。
【図15】実施例におけるOG827を用いたPCRの電気泳動の結果を示す。
【図16】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【図17】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【図18】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【図19】本発明のプライマーで増幅した特定マーカーの塩基配列を示す。
【発明を実施するための形態】
【0039】
次に、本発明を実施例に基づいて具体的に説明するが、本発明は、以下の実施例によって何ら限定されるものではない。
【実施例】
【0040】
国内で育成されたオーチャードグラスのアキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種から、CTAB法を用いて、ゲノムDNAを抽出した。
【0041】
抽出したDNA溶液は、滅菌水でDNA濃度を20ng/μlに調整し、10個体を混合し、バルクにしたものを、PCR用のテンプレートDNAとして用いた。
【0042】
本実施例で使用した機器は、以下の通りである。
すなわち、本実施例では、T GRADIENT Themocycler(Biometra)、TaKaRa PCR Thermal Cycler TP600(タカラバイオ株式会社)、i Cycler(BIO−RAD)、及び、Gene Amp PCR System 9700(ABI)、DNAシーケンシングシステムLIC−4200L(s)(LI−COR)を用いた。
【0043】
<50%アクリルアミドゲル>
本実施例で使用した試薬は、以下の通りである。
アクリルアミドゲルとして、尿素(和光純薬工業株式会社)、Long Ranger Gel solution DNA Sequencing用(タカラバイオ株式会社)、10xTBE buffer、10%APS、TEMED(和光純薬工業株式会社)、を用いた。
【0044】
<PCR反応液>
PCR反応液として、Gene Taq NT(和光純薬工業株式会社)もしくはTaq DNA Polymerase(BIO NEER)、1pmol/μl M13 Forward(−29)Primer:IRD700もしくはIRD800の蛍光標識を含む(日清紡)、を用いた。サイズマーカーとして、50−350bp SIZING STANDARD−BULK(LI−COR)を使用した。本発明では、LI−CORのプロトコールに基づいて、ゲルと色素マーカーの作製を行った。
【0045】
<PCR反応液:計10μlの調製>
PCR反応液の調製は、以下の通りとした。
トールフェスク対象品種から抽出したバルクDNA:1μl
10xGene Taq Universal buffer:1μl
2.5mM dNTP Mixture:0.8μl
ddH2O:6.5μl
Primer Forward(20pmol/μl):0.06μl
Primer Reverse(20pmol/μl):0.3μl
M13 Forward(−29) Primer:0.3μl
Gene Taq NT(5 unit/μl):0.1μl
BIO NEERのTaq DNA Polymeraseを使用する場合にも、同様にPCR反応液を調製した。
【0046】
<PCR条件>
PCR条件は、以下の通りとした。
95℃1分−65℃1分−72℃1分30秒(2サイクル)95℃1分−65℃1分−72℃1分30秒(10サイクル。1サイクルごとに65℃を1℃ずつ下げていく)95℃1分−55℃1分−72℃1分30秒(30サイクル)で反応させた。PCR増幅産物は、色素マーカー5μlを加え、90℃3分のディネーチャーを行った後、遮光し、氷上で1時間以上静置させることで安定させた後、アクリルアミドゲルを使用して、電気泳動を行い、マーカーの増幅を確認した。
【0047】
本実施例では、特に記載しない限り、オーチャードグラスのアキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種を、テンプレートとして使用した。
【0048】
本実施例では、オーチャードグラスの14品種それぞれのバルクしたDNAを、4サンプル使用して、電気泳動を行い、14品種を同時に比較した(図1〜15)。
【0049】
プライマー「OG493」を使用し、PCRを行った。その電気泳動の結果を図1に示す。このプライマー対は、145〜175bpの間で、アキミドリIIに特異的な増幅を示し、アキミドリIIの識別に有効であった。プライマー「OG954」を併用することで、識別精度が向上した。
【0050】
プライマー「OG954」を使用し、PCRを行った。その電気泳動の結果を図2に示す。このプライマー対は、175〜200bpの間で、アキミドリII特有の増幅を示し、175bp付近で、バッカスに特異的な増幅を示し、2品種の識別に有効であった。アキミドリIIについては、プライマー「OG493」を併用することで、識別精度が向上した。
【0051】
プライマー「OG785」を使用し、PCRを行った。その電気泳動の結果を図3に示す。このプライマー対は、176bp付近で、キタミドリに特異的な増幅を示し、キタミドリの識別に有効であった。
【0052】
プライマー「OG670」を使用し、PCRを行った。その電気泳動の結果を図4に示す。このプライマー対は、100bp付近で、ナツミドリに特異的な増幅を示し、ナツミドリの識別に有効であった。
【0053】
プライマー「OG474」を使用し、PCRを行った。その電気泳動の結果を図5に示す。このプライマー対は、145〜175bpの間で、オカミドリに特異的な増幅を示し、オカミドリの識別に有効であった。キタミドリによく似たサイズの増幅が見られることから、キタミドリのバルクDNAをスタンダードとして、同時に泳動し、比較することが必要になる。
【0054】
プライマー「OG654」を使用し、PCRを行った。その電気泳動の結果を図6に示す。このプライマー対は、145bp付近で、ワセミドリに特異的な増幅を示し、ワセミドリの識別に有効であった。
【0055】
プライマー「OG202」を使用し、PCRを行った。その電気泳動の結果を図7に示す。このプライマー対では、230bp付近で、ハルジマンに特異的な増幅を示し、145〜175bpの間に、トヨミドリ特有の増幅を示し、これらの2品種の識別に有効であった。
【0056】
プライマー「OG264」を使用し、PCRを行った。その電気泳動の結果を図8に示す。このプライマー対は、230から255bpの間で、マキバミドリに特異的な増幅を示し、マキバミドリの識別に有効であった。
【0057】
プライマー「OG261」を使用し、PCRを行った。その電気泳動の結果を図9に示す。このプライマー対は、230bp付近で、ベンチマークに特異的な増幅を示し、ベンチマークの識別に有効であった。
【0058】
プライマー「OG503」を使用し、PCRを行った。その電気泳動の結果を図10に示す。このプライマー対は、200bp付近で、はるねみどりに特異的な増幅を示し、はるねみどりの識別に有効であった。
【0059】
プライマー「OG357」を使用し、PCRを行った。その電気泳動の結果を図11に示す。このプライマー対は、145bp付近の増幅パターンの違いによって、フロンティア及びポトマックの識別に有効であった。プライマー「OG806」及び「OG965」を併用することで、精度を向上させることができる。
【0060】
プライマー「OG806」を使用し、PCRを行った。その電気泳動の結果を図12に示す。このプライマー対は、145bp付近の増幅パターンの違いによって、フロンティア及びポトマックの識別を行うことができた。プライマー「OG357」及び「OG965」を併用することで、精度を向上させることができる。
【0061】
プライマー「OG965」を使用し、PCRを行った。その電気泳動の結果を図13に示す。このプライマー対は、175bp付近の増幅でフロンティアとポトマック間の区別性を示し、フロンティア及びポトマックの識別に有効であった。プライマー「OG357」及び「OG806」を併用することで、精度を向上させることができる。
【0062】
プライマー「OG757」を使用し、PCRを行った。その電気泳動の結果を図14に示す。このプライマー対は、120bp付近で、まきばたろうに特異的な増幅を示し、まきばたろうの識別に有効であった。プライマー「OG827」を併用することで、識別精度が向上した。
【0063】
「OG827」を使用しPCRを行った。その電気泳動の結果を図15に示す。このプライマー対は、204bp付近で、まきばたろうに特異的な増幅を示し、まきばたろうの識別に有効であった。プライマー「OG757」を併用することで、識別精度が向上した。本発明のプライマーで増幅した特定マーカー遺伝子の塩基配列を、図16〜19に示す。
【産業上の利用可能性】
【0064】
以上詳述したように、本発明は、オーチャードグラスの品種識別に有用なSSRプライマー対及びその利用に係るものであり、本発明により、オーチャードグラス14品種の特定のSSR領域を増幅させるための遺伝子増幅用プライマーのFプライマー及びRプライマー対を提供することができる。また、本発明は、単数又は複数のプライマー対を使用したPCRにより識別対象の遺伝子を増幅させてなるマーカー遺伝子を提供することができ、そのマーカー遺伝子のサイズ及びバンドパターンを検証することにより、オーチャードグラスの品種識別を行うことができる。本発明により、オーチャードグラスの14品種相互での品種識別を行うことができる。本発明は、短い時間で、正確なオーチャードグラスの品種識別を可能にする新しい品種識別方法を提供するものとして有用である。
【符号の説明】
【0065】
1 アキミドリII
2 キタミドリ
3 ナツミドリ
4 バッカス
5 オカミドリ
6 ワセミドリ
7 ハルジマン
9 マキバミドリ
10 トヨミドリ
11 ベンチマーク
12 はるねみどり
13 フロンティア
14 ポトマック
15 まきばたろう
【特許請求の範囲】
【請求項1】
オーチャードグラスの品種識別用のプライマーであって、オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマー対。
【請求項2】
オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマーのF(Forward)プライマー及びR(Reverse)プライマーからなる、請求項1に記載のプライマー対。
【請求項3】
オーチャードグラスのゲノム上におけるSSR領域の両端の塩基配列を用いて設計した遺伝子増幅用プライマー対であって、配列表の配列番号1〜15のF(Forward)プライマー及び配列番号16〜30のR(Reverse)プライマーを1対とするプライマー対である、請求項1に記載のプライマー対。
【請求項4】
請求項2に記載のプライマー対の単数又は複数の組合せからなることを特徴とするオーチャードグラスの品種識別用プライマーセット。
【請求項5】
オーチャードグラスのゲノム上におけるSSR領域を増幅する請求項1から4のいずれかに記載のプライマーからPCR増幅させた特定の増幅産物からなることを特徴とするマーカー遺伝子。
【請求項6】
請求項5に記載のマーカー遺伝子であって、配列表の配列番号31〜45のいずれかの塩基配列を有することを特徴とするマーカー遺伝子。
【請求項7】
請求項5又は6に記載のマーカー遺伝子を使用し、識別対象のオーチャードグラスDNAのPCR増幅の増幅産物の多型を確認することで品種の識別を行うことを特徴とするオーチャードグラスの品種識別方法。
【請求項8】
識別対象のオーチャードグラス遺伝子のPCR増幅産物のサイズ又はバンドパターンに基づいて、品種の識別を行うことを特徴とするオーチャードグラス品種識別方法。
【請求項9】
対象品種のバルクDNAをテンプレートDNAとして使用したオーチャードグラス遺伝子のPCRによる増幅を行い、同時に、数品種の識別を行う、請求項7又は8に記載の方法。
【請求項10】
アキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種からなるオーチャードグラス品種を識別する、請求項7〜9のいずれかに記載の品種識別方法。
【請求項1】
オーチャードグラスの品種識別用のプライマーであって、オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマー対。
【請求項2】
オーチャードグラスのゲノム上におけるSSR(Simple Sequence Repeats)領域を増幅させるための遺伝子増幅用プライマーのF(Forward)プライマー及びR(Reverse)プライマーからなる、請求項1に記載のプライマー対。
【請求項3】
オーチャードグラスのゲノム上におけるSSR領域の両端の塩基配列を用いて設計した遺伝子増幅用プライマー対であって、配列表の配列番号1〜15のF(Forward)プライマー及び配列番号16〜30のR(Reverse)プライマーを1対とするプライマー対である、請求項1に記載のプライマー対。
【請求項4】
請求項2に記載のプライマー対の単数又は複数の組合せからなることを特徴とするオーチャードグラスの品種識別用プライマーセット。
【請求項5】
オーチャードグラスのゲノム上におけるSSR領域を増幅する請求項1から4のいずれかに記載のプライマーからPCR増幅させた特定の増幅産物からなることを特徴とするマーカー遺伝子。
【請求項6】
請求項5に記載のマーカー遺伝子であって、配列表の配列番号31〜45のいずれかの塩基配列を有することを特徴とするマーカー遺伝子。
【請求項7】
請求項5又は6に記載のマーカー遺伝子を使用し、識別対象のオーチャードグラスDNAのPCR増幅の増幅産物の多型を確認することで品種の識別を行うことを特徴とするオーチャードグラスの品種識別方法。
【請求項8】
識別対象のオーチャードグラス遺伝子のPCR増幅産物のサイズ又はバンドパターンに基づいて、品種の識別を行うことを特徴とするオーチャードグラス品種識別方法。
【請求項9】
対象品種のバルクDNAをテンプレートDNAとして使用したオーチャードグラス遺伝子のPCRによる増幅を行い、同時に、数品種の識別を行う、請求項7又は8に記載の方法。
【請求項10】
アキミドリII、キタミドリ、ナツミドリ、バッカス、オカミドリ、ワセミドリ、ハルジマン、マキバミドリ、トヨミドリ、ベンチマーク、はるねみどり、フロンティア、ポトマック、まきばたろう、の14品種からなるオーチャードグラス品種を識別する、請求項7〜9のいずれかに記載の品種識別方法。
【図16】


【図17】


【図18】


【図19】


【図1】


【図2】


【図3】


【図4】


【図5】


【図6】


【図7】


【図8】


【図9】


【図10】


【図11】


【図12】


【図13】


【図14】


【図15】




【図17】


【図18】


【図19】


【図1】


【図2】


【図3】


【図4】


【図5】


【図6】


【図7】


【図8】


【図9】


【図10】


【図11】


【図12】


【図13】


【図14】


【図15】


【公開番号】特開2011−211948(P2011−211948A)
【公開日】平成23年10月27日(2011.10.27)
【国際特許分類】
【出願番号】特願2010−82482(P2010−82482)
【出願日】平成22年3月31日(2010.3.31)
【出願人】(501025388)社団法人日本草地畜産種子協会 (11)
【Fターム(参考)】
【公開日】平成23年10月27日(2011.10.27)
【国際特許分類】
【出願日】平成22年3月31日(2010.3.31)
【出願人】(501025388)社団法人日本草地畜産種子協会 (11)
【Fターム(参考)】
[ Back to top ]

